Los resultados del trabajo, publicados y destacados en la portada del último número de la revista »Proceedings of the National Academy of Sciences» (PNAS), abren la vía para seguir profundizando en el funcionamiento genético de estas potenciales biofactorías, según el CSIC.
Los investigadores pudieron definir el transcriptoma a través de una metodología basada en la secuenciación masiva de ARN que ha permitido identificar las posiciones del genoma a partir del inicio de la transcripción del ADN.
La investigadora del CSIC en el Instituto de Bioquímica Vegetal y Fotosíntesis, Alicia Muro, ha explicado que, para alcanzar un resultado, «se han asignado todas las posiciones en las que se inicia la transcripción a lo largo del genoma de la bacteria». «Esta técnica, extraordinariamente potente, se ha empleado, por ejemplo, para definir el transcriptoma de algunas bacterias patógenas como la »Helicobacter pylori»», precisa.
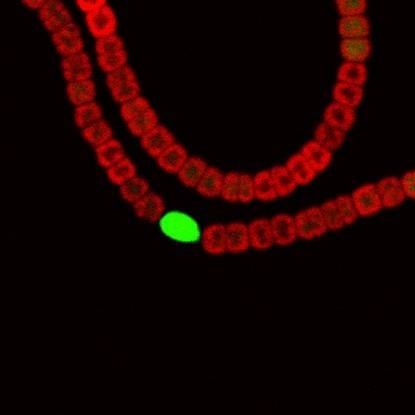
Las cianobacterias son organismos modelo para estudiar la fotosíntesis oxigénica, pero también se consideran útiles porque son biofactorías y productoras de biocombustibles en potencia. Además, las »Anabaena» son de las pocas cianobacterias capaces de fijar nitrógeno atmosférico. Este proceso se lleva a cabo en unas células especializadas y diferenciadas llamadas heterocistos, que se encuentran situadas en los filamentos de estas cianobacterias.
El estudio, que se ha llevado a cabo en colaboración con un equipo dirigido por Wolfgang R. Hess, de la Universidad Albert Ludwig en Friburgo (Alemania), abre también la vía para el análisis detallado a nivel molecular de la expresión de los genes implicados, no sólo en la adaptación a la deficiencia de nitrógeno, sino en cualquier proceso, ya que define los promotores y los inicios de la transcripción a lo largo de todo el genoma de »Anabaena».